for (pkg in c("tidyverse", "gapminder", "ggrepel")) {
if (!require(pkg, character.only = TRUE)) install.packages(pkg)
}Streudiagramme mit vielen Datenpunkten profitieren oft von Textlabels, die einzelne Beobachtungen identifizieren - Laendernamen, Gen-IDs oder Probenbezeichnungen. Der naheliegendste Ansatz ist geom_text(), aber sobald die Anzahl der beschrifteten Punkte ueber eine Handvoll hinausgeht, ueberlappen sich die Labels gegenseitig und verdecken die Datenpunkte, sodass der Plot unleserlich wird.
Das {ggrepel}-Paket loest dieses Problem mit zwei Drop-in-Ersetzungen: geom_text_repel() und geom_label_repel(). Beide verwenden einen iterativen Algorithmus, der Labels voneinander und von den Datenpunkten wegschiebt und duenne Linien-Segmente zeichnet, die jedes Label mit seinem Punkt verbinden. Da die Funktionen dieselbe Aesthetik-Schnittstelle wie geom_text() und geom_label() haben, reicht es, den Funktionsnamen auszutauschen.
In diesem Kapitel verwendet man den gapminder-Datensatz fuer das Jahr 2007 und stellt das BIP pro Kopf gegen die Lebenserwartung fuer alle 142 Laender dar - ein dichtes Streudiagramm, bei dem die automatische Label-Platzierung einen echten Unterschied macht.
Setup
Man filtert die gapminder-Daten auf das Jahr 2007 und behaelt alle Laender. Da das BIP pro Kopf mehrere Groessenordnungen umfasst (von wenigen hundert bis ueber 40.000 USD), wird durchgehend eine logarithmische x-Achse verwendet.
# A tibble: 142 × 6
country continent year lifeExp pop gdpPercap
<fct> <fct> <int> <dbl> <int> <dbl>
1 Afghanistan Asia 2007 43.8 31889923 975.
2 Albania Europe 2007 76.4 3600523 5937.
3 Algeria Africa 2007 72.3 33333216 6223.
4 Angola Africa 2007 42.7 12420476 4797.
5 Argentina Americas 2007 75.3 40301927 12779.
6 Australia Oceania 2007 81.2 20434176 34435.
7 Austria Europe 2007 79.8 8199783 36126.
8 Bahrain Asia 2007 75.6 708573 29796.
9 Bangladesh Asia 2007 64.1 150448339 1391.
10 Belgium Europe 2007 79.4 10392226 33693.
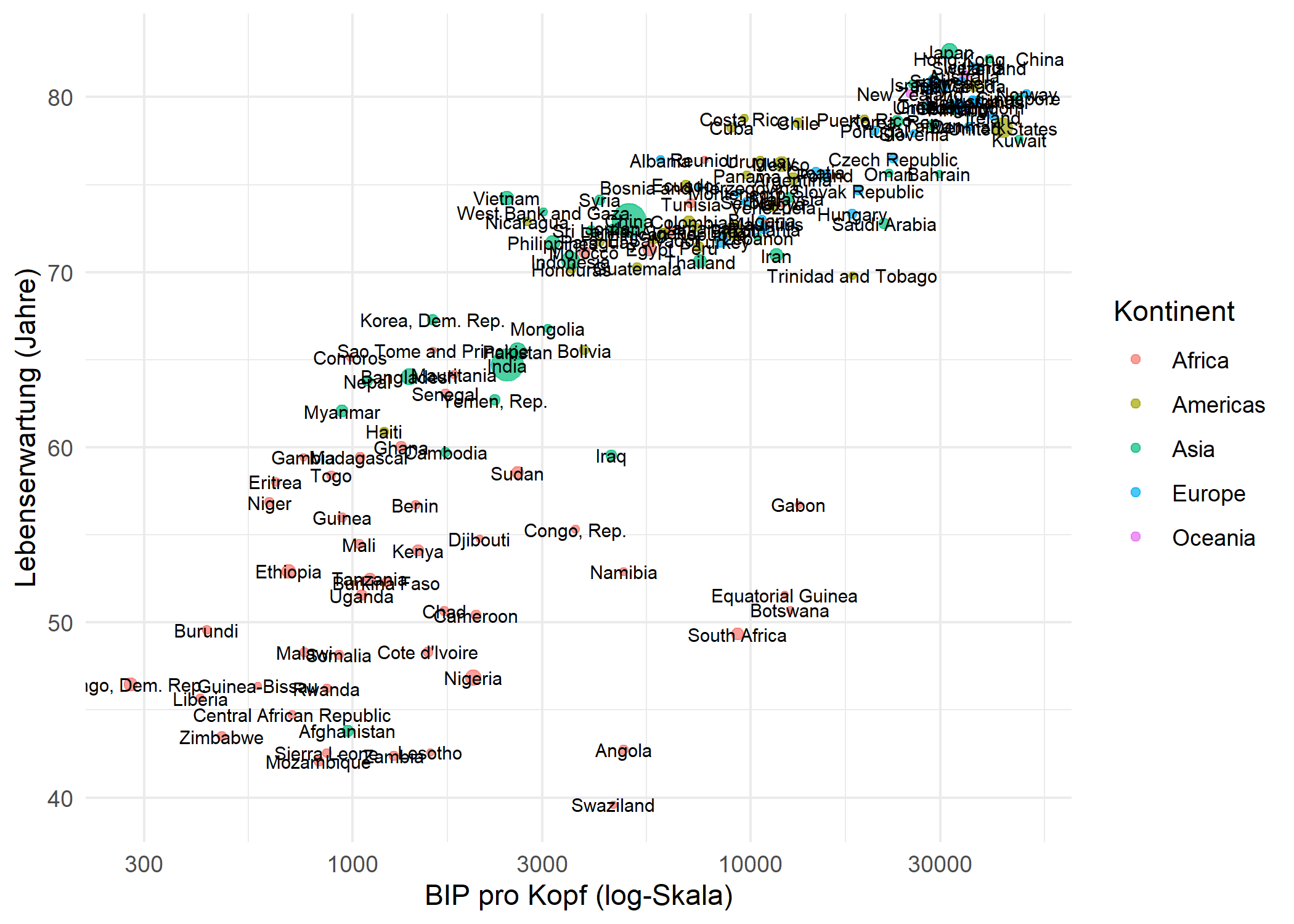
# ℹ 132 more rowsUm das Labeling-Problem zu veranschaulichen, erstellen wir hier ein Streudiagramm mit geom_text() - jeder Laendername wird direkt an seinem Datenpunkt platziert:
ggplot(dat, aes(x = gdpPercap, y = lifeExp)) +
geom_point(aes(size = pop, color = continent), alpha = 0.7) +
geom_text(aes(label = country), size = 2.5) +
scale_x_log10() +
scale_size_continuous(guide = "none") +
labs(
x = "BIP pro Kopf (log-Skala)",
y = "Lebenserwartung (Jahre)",
color = "Kontinent"
) +
theme_minimal()Das Ergebnis ist ein unleserliches Durcheinander: Labels ueberlappen sich gegenseitig und verdecken die Punkte. Genau zur Loesung dieses Problems wurde ggrepel entwickelt.
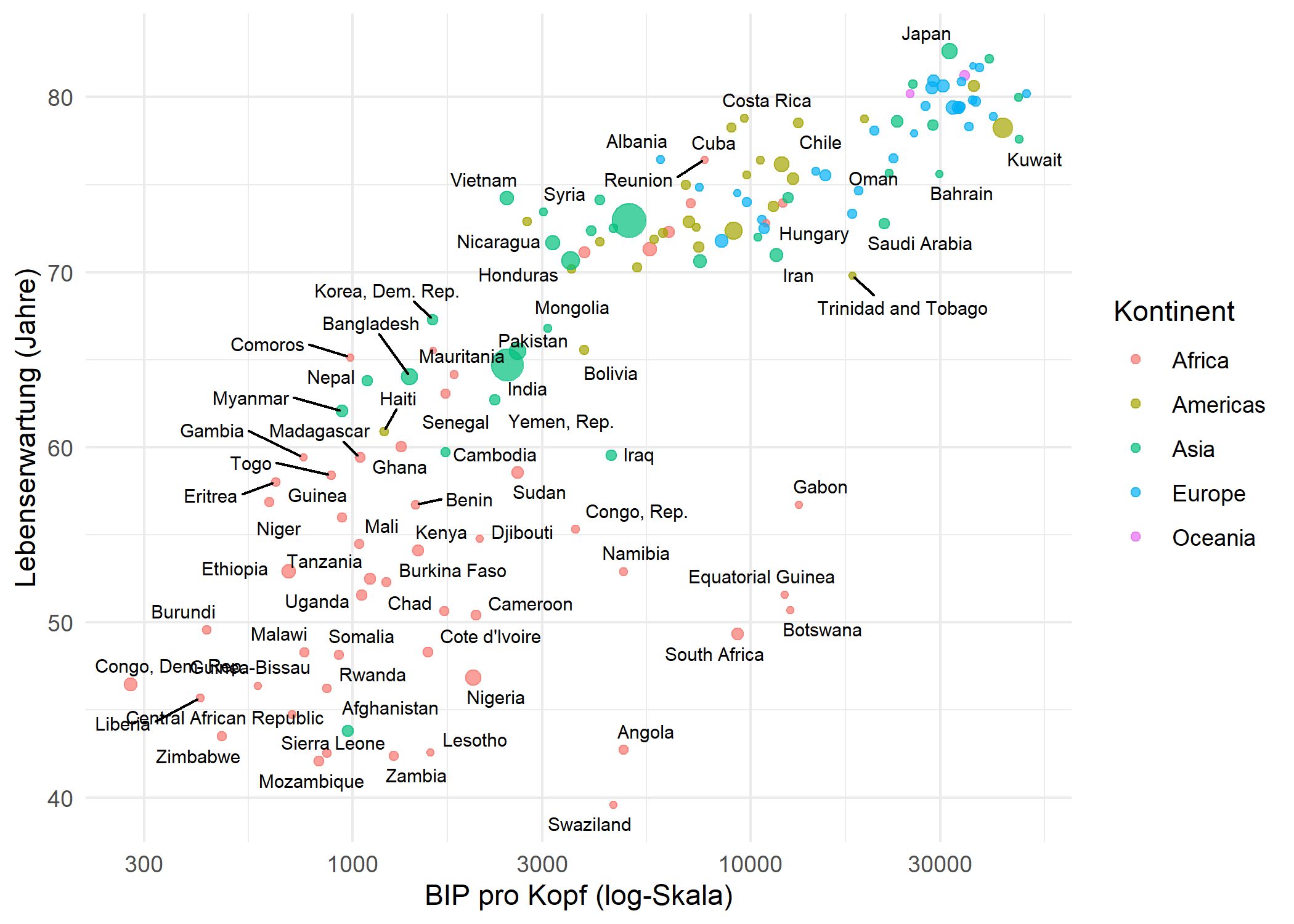
geom_text_repel
Man ersetzt einfach geom_text() durch geom_text_repel(). Die Funktion positioniert Labels automatisch so um, dass sie sich nicht ueberlappen, und zeichnet ein kleines Liniensegment von jedem Label zu seinem Datenpunkt:
ggplot(dat, aes(x = gdpPercap, y = lifeExp)) +
geom_point(aes(size = pop, color = continent), alpha = 0.7) +
geom_text_repel(aes(label = country), size = 2.5) +
scale_x_log10() +
scale_size_continuous(guide = "none") +
labs(
x = "BIP pro Kopf (log-Skala)",
y = "Lebenserwartung (Jahre)",
color = "Kontinent"
) +
theme_minimal()Warning: ggrepel: 68 unlabeled data points (too many overlaps). Consider
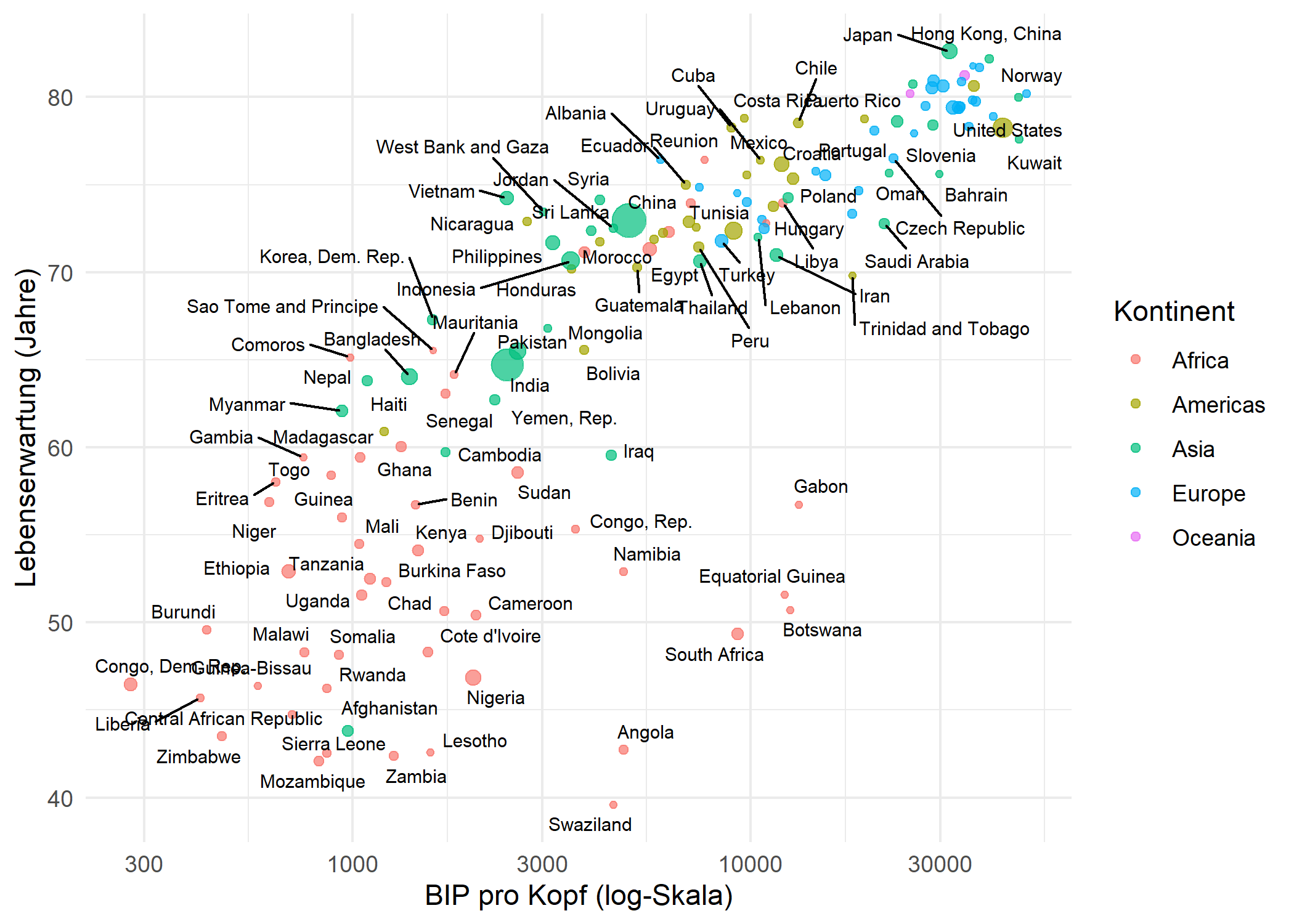
increasing max.overlapsStandardmaessig unterdrueckt geom_text_repel() Labels, wenn mehr als 10 in derselben Region ueberlappen wuerden (gesteuert durch max.overlaps). Mehrere Parameter helfen bei der Feinabstimmung der Platzierung:
-
max.overlaps- Maximale Anzahl ueberlappender Labels, bevor ein Label ausgeblendet wird. Der Standard ist 10; man setztInf, um alle Labels unabhaengig von Ueberlappungen anzuzeigen. -
box.padding- Zusaetzlicher Abstand um die Bounding Box jedes Labels (Standard 0.25 Zeilen). Erhoehen fuer mehr Abstand zwischen Labels. -
point.padding- Mindestabstand zwischen einem Label und seinem Datenpunkt (Standard 0). -
min.segment.length- Segmente kuerzer als dieser Wert werden ausgeblendet (Standard 0.5 Zeilen). Auf 0 setzen, um Segmente immer anzuzeigen. -
seed- Der Repulsion-Algorithmus hat eine stochastische Komponente. Durch Setzen eines Seeds erhaelt man bei jedem Rendern dieselben Label-Positionen.
ggplot(dat, aes(x = gdpPercap, y = lifeExp)) +
geom_point(aes(size = pop, color = continent), alpha = 0.7) +
geom_text_repel(
aes(label = country),
size = 2.5,
max.overlaps = 20,
seed = 42
) +
scale_x_log10() +
scale_size_continuous(guide = "none") +
labs(
x = "BIP pro Kopf (log-Skala)",
y = "Lebenserwartung (Jahre)",
color = "Kontinent"
) +
theme_minimal()Warning: ggrepel: 35 unlabeled data points (too many overlaps). Consider
increasing max.overlapsgeom_label_repel
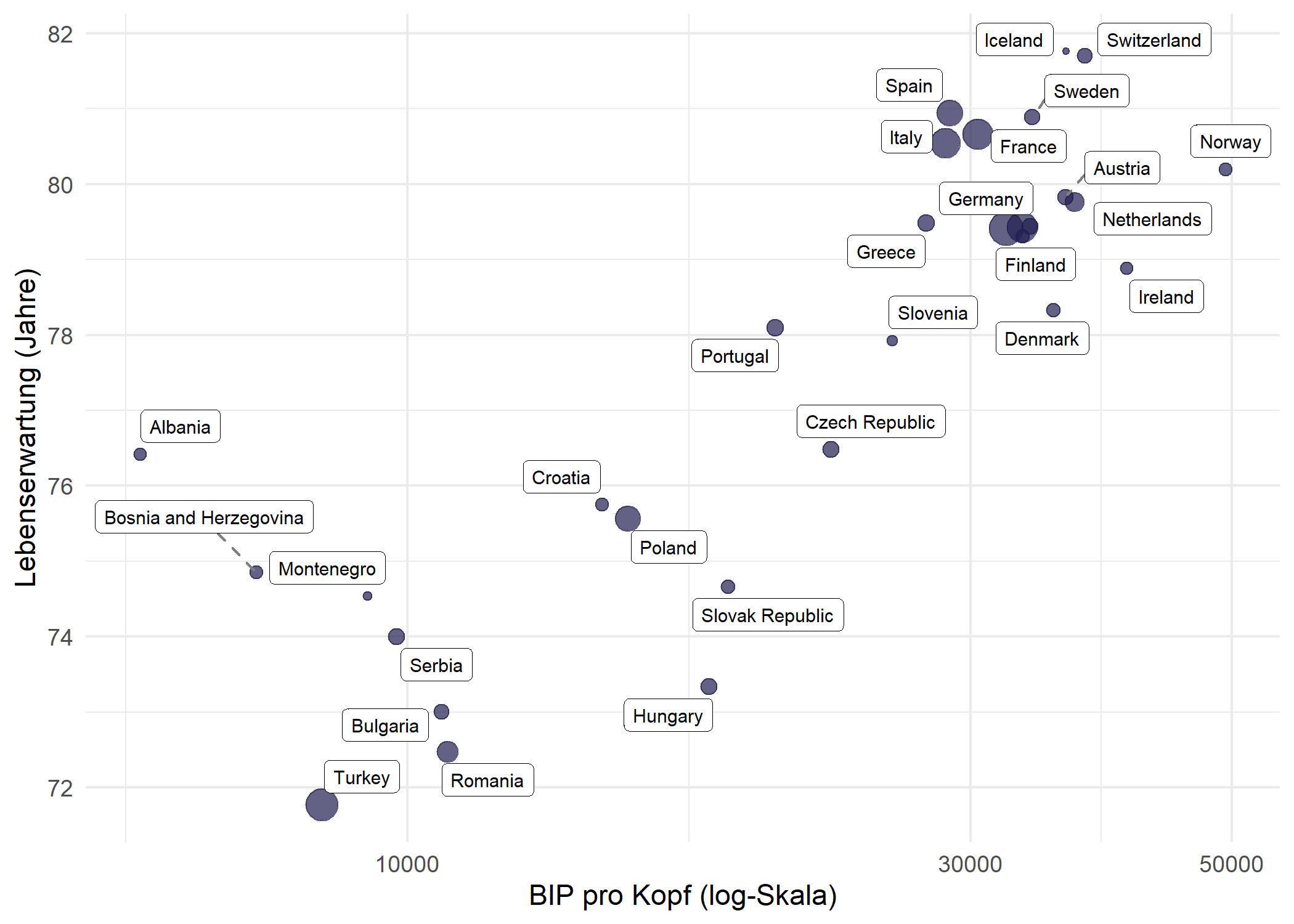
Waehrend geom_text_repel() einfachen Text zeichnet, platziert geom_label_repel() den Text in einem gefuellten Rechteck - nuetzlich, wenn Labels sich von einem unruhigen Hintergrund abheben muessen. Die Verbindungssegmente lassen sich unabhaengig gestalten:
dat_small <- dat %>%
filter(continent == "Europe")
ggplot(dat_small, aes(x = gdpPercap, y = lifeExp)) +
geom_point(aes(size = pop), color = "#201E50", alpha = 0.7) +
geom_label_repel(
aes(label = country),
size = 2.5,
fill = "white",
label.size = 0.2,
segment.color = "grey50",
segment.linetype = "dashed",
seed = 42
) +
scale_x_log10() +
scale_size_continuous(guide = "none") +
labs(
x = "BIP pro Kopf (log-Skala)",
y = "Lebenserwartung (Jahre)"
) +
theme_minimal()Warning: ggrepel: 2 unlabeled data points (too many overlaps). Consider
increasing max.overlapsDa das Labeln aller 142 Laender auf einmal selbst mit Repulsion ueberfordernd wirkt, ist eine Filterung auf einen einzelnen Kontinent (hier Europa mit 30 Laendern) fuer geom_label_repel() deutlich effektiver.
Selektives Labeling
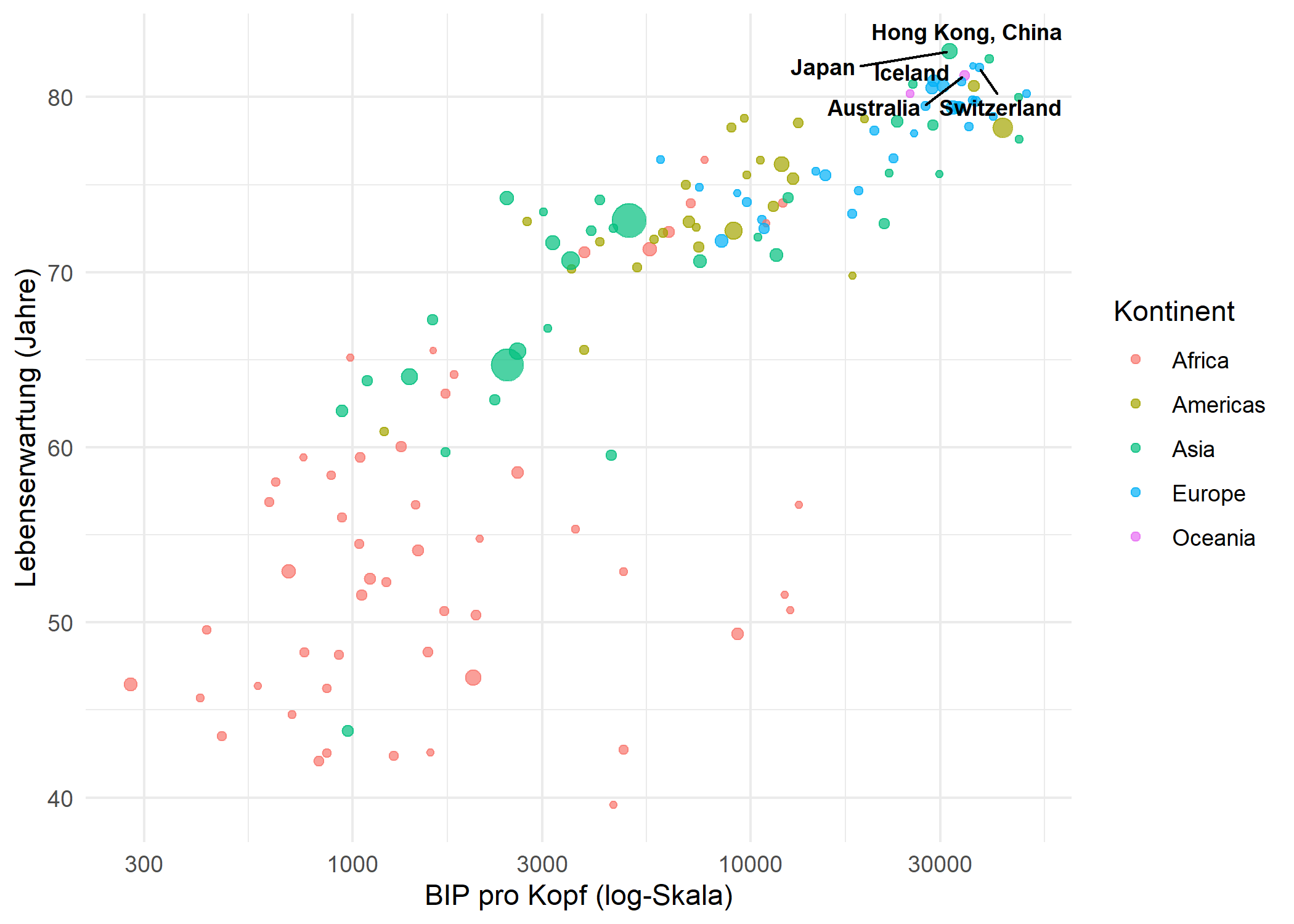
In vielen Situationen ist es weder noetig noch wuenschenswert, jeden Punkt zu beschriften. Eine gaengige Strategie besteht darin, nur die interessantesten Beobachtungen zu beschriften - zum Beispiel die Laender mit der hoechsten Lebenserwartung - und den Rest als unbeschriftete Punkte zu belassen. So bleibt der Plot uebersichtlich und hebt gleichzeitig die wichtigsten Daten hervor.
Der Ansatz ist einfach: Man erstellt eine Hilfsspalte, die den Laendernamen fuer Punkte enthaelt, die beschriftet werden sollen, und NA fuer alle anderen. geom_text_repel() ueberspringt NA-Werte bei na.rm = TRUE:
top5 <- dat %>%
slice_max(lifeExp, n = 5) %>%
pull(country)
dat_labeled <- dat %>%
mutate(label_col = if_else(country %in% top5, as.character(country), NA_character_))
ggplot(dat_labeled, aes(x = gdpPercap, y = lifeExp)) +
geom_point(aes(size = pop, color = continent), alpha = 0.7) +
geom_text_repel(
aes(label = label_col),
size = 3,
fontface = "bold",
seed = 42,
na.rm = TRUE
) +
scale_x_log10() +
scale_size_continuous(guide = "none") +
labs(
x = "BIP pro Kopf (log-Skala)",
y = "Lebenserwartung (Jahre)",
color = "Kontinent"
) +
theme_minimal()Diese Technik skaliert gut: Man kann Ausreisser, Punkte ueber einem Schwellenwert oder jede durch eine logische Bedingung definierte Teilmenge beschriften - alles ohne den zugrundeliegenden Datensatz zu veraendern.
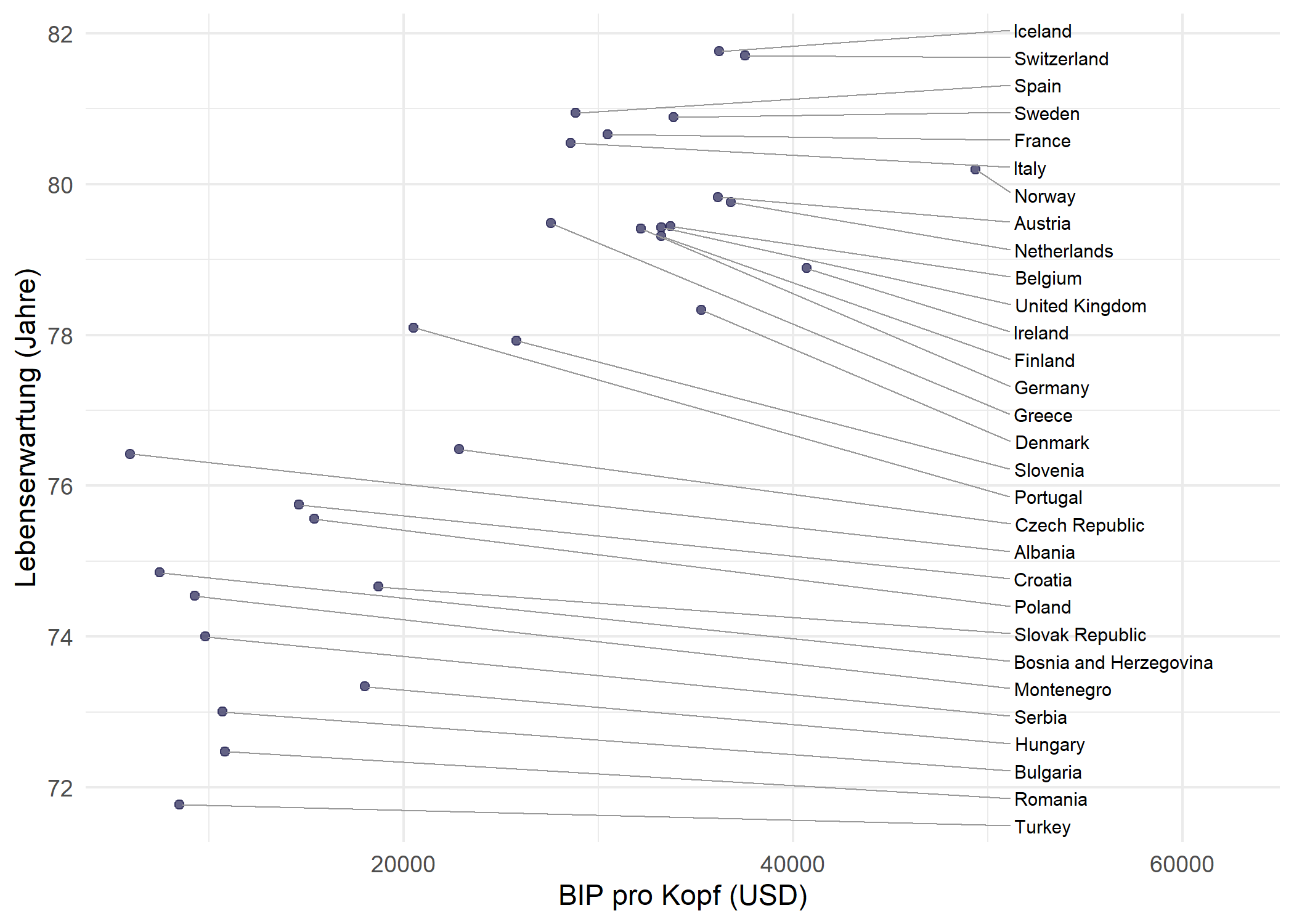
Seitenausgerichtete Labels
Ein besonders aufgeraeumter Labeling-Stil platziert alle Labels auf einer Seite des Plots, vertikal ausgerichtet. Das vermeidet das verstreute Erscheinungsbild frei abgestossener Labels und funktioniert gut, wenn die Anzahl der Punkte ueberschaubar ist. Die Schluesselparameter sind:
-
direction = "y"- beschraenkt die Label-Bewegung auf die vertikale Achse, sodass Labels auf derselben x-Position bleiben -
hjust = 0- richtet den Labeltext linksbuendig aus -
nudge_x- verschiebt alle Labels um einen festen Abstand nach rechts von ihren Datenpunkten -
expandauf der x-Achse - schafft genuegend Platz auf der rechten Seite fuer die Labels
dat_europe <- dat %>%
filter(continent == "Europe")
max_gdp <- max(dat_europe$gdpPercap)
ggplot(dat_europe, aes(x = gdpPercap, y = lifeExp)) +
geom_point(color = "#201E50", alpha = 0.7) +
geom_text_repel(
aes(label = country),
size = 2.5,
direction = "y",
hjust = 0,
nudge_x = max_gdp - dat_europe$gdpPercap + 2000,
segment.size = 0.3,
segment.color = "grey60",
seed = 42
) +
scale_x_continuous(
name = "BIP pro Kopf (USD)",
expand = expansion(mult = c(0.05, 0.3))
) +
labs(y = "Lebenserwartung (Jahre)") +
theme_minimal()Der Trick ist, nudge_x pro Punkt als max(x) - x + offset zu berechnen, sodass jedes Label unabhaengig von der Position seines Datenpunkts an derselben x-Position landet. In Kombination mit direction = "y" breiten sich die Labels nur vertikal von diesem Ankerpunkt aus und bilden eine ordentliche Spalte, die durch gerade horizontale Segmente mit ihren Punkten verbunden ist.
Bei Hunderten von Labels kann der Repulsion-Algorithmus langsam werden. Zwei Parameter helfen bei der Steuerung der Rechenzeit: max.overlaps begrenzt, wie viele ueberlappende Labels versucht werden (der Rest wird ausgeblendet), und max.time setzt ein Zeitlimit fuer den Algorithmus in Sekunden (Standard 0.5). Fuer sehr dichte Plots ist selektives Labeling wie oben gezeigt meist der bessere Ansatz.
Zitat
@online{schmidt2026,
author = {{Dr. Paul Schmidt}},
publisher = {BioMath GmbH},
title = {7. ggrepel},
date = {2026-03-12},
url = {https://biomathcontent.netlify.app/de/content/ggplot2/07_ggrepel.html},
langid = {de}
}