for (pkg in c("tidyverse", "gapminder", "showtext", "ggtext", "patchwork", "cowplot")) {
if (!require(pkg, character.only = TRUE)) install.packages(pkg)
}
showtext::showtext_opts(dpi = 300)Wissenschaftliche Publikationen und Praesentationen erfordern oft mehrere zusammengehoerige Plots in einer einzigen Abbildung - ein Balkendiagramm neben einem Dumbbell Plot oder eine Zeitreihe ueber einem Streudiagramm. Waehrend facet_wrap() Faelle abdeckt, in denen derselbe Plottyp fuer verschiedene Teilmengen wiederholt wird, kann es keine grundlegend verschiedenen Plottypen oder Datensaetze kombinieren. Das {patchwork}-Paket von Thomas Lin Pedersen fuellt diese Luecke mit einer intuitiven operatorbasierten Syntax zum Zusammensetzen von ggplot2-Objekten.
In diesem Kapitel erstellen wir das Balkendiagramm und den Dumbbell Plot aus Kapitel 5 neu und kombinieren sie mit patchworks Layout-Operatoren zu Multi-Panel-Abbildungen.
Setup
Wir reproduzieren die Plots aus Kapitel 5. Der Code ist eingeklappt, da er eine Wiederholung frueheren Materials ist:
show/hide code
sysfonts::font_add_google("Kanit", "kanit")
showtext::showtext_auto()
dat <- gapminder::gapminder %>%
filter(year == 1952 | year == 2007) %>%
filter(country %in% c(
"Canada", "Germany", "Japan",
"Netherlands", "Nigeria", "Vietnam", "Zimbabwe"
)) %>%
mutate(year = as.factor(year)) %>%
droplevels()
sorted_countries <- dat %>%
filter(year == "2007") %>%
arrange(lifeExp) %>%
pull(country) %>%
as.character()
dat <- dat %>%
mutate(country = fct_relevel(country, sorted_countries))
year_colors <- c("1952" = "#F7AA59", "2007" = "#37A9E1")
theme_nature <- function(base_size = 12) {
theme_minimal(base_size = base_size) +
theme(
text = element_text(family = "kanit"),
plot.title.position = "plot",
plot.title = element_text(size = 15, face = "bold"),
plot.subtitle = ggtext::element_textbox_simple(
size = 10, margin = margin(0, 0, 10, 0)
),
axis.line.y = element_blank(),
axis.text.x = element_text(color = "#AAAAAA"),
axis.ticks.x = element_line(color = "#AAAAAA", linewidth = 0.4),
axis.ticks.length.x = unit(4, "pt"),
axis.line.x = element_line(color = "black", linewidth = 0.6),
legend.position = "top",
legend.box.just = "left",
legend.justification = "left",
legend.title = element_text(face = "bold"),
legend.key.size = unit(0.4, "cm"),
legend.margin = margin(-5, 0, 0, 0),
panel.grid.minor = element_blank(),
panel.grid.major.y = element_blank(),
panel.grid.major.x = element_line(
linetype = "dotted", color = "#AAAAAA", linewidth = 0.3
)
)
}
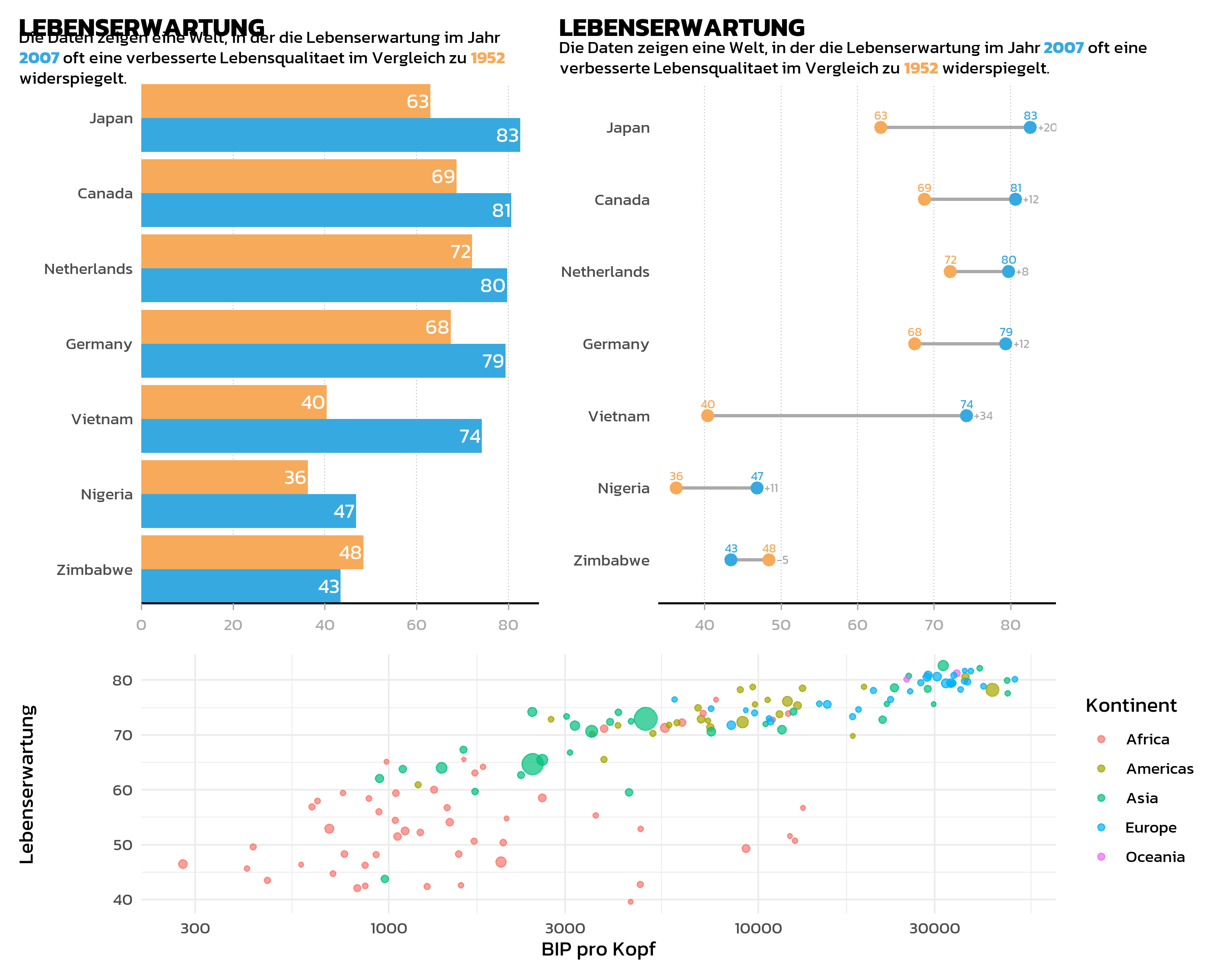
long_subtitle <- "Die Daten zeigen eine Welt, in der die Lebenserwartung im Jahr <b style='color:#37A9E1;'>2007</b> oft eine verbesserte Lebensqualitaet im Vergleich zu <b style='color:#F7AA59;'>1952</b> widerspiegelt."
# Balkendiagramm
p_bar <- ggplot(data = dat) +
aes(x = lifeExp, y = country, fill = fct_rev(year)) +
geom_col(position = position_dodge()) +
geom_text(
mapping = aes(label = round(lifeExp), group = fct_rev(year)),
position = position_dodge(width = 0.9),
hjust = 1.1, color = "white", family = "kanit"
) +
scale_y_discrete(name = NULL, expand = c(0, 0)) +
scale_x_continuous(name = NULL, expand = expansion(mult = c(0, 0.05))) +
scale_fill_manual(
guide = "none", name = "Year",
limits = names(year_colors), values = year_colors
) +
labs(title = "LEBENSERWARTUNG", subtitle = long_subtitle) +
theme_nature()
# Dumbbell Plot
dat_wide <- dat %>%
select(country, year, lifeExp) %>%
pivot_wider(
names_from = year, values_from = lifeExp, names_prefix = "year_"
) %>%
mutate(
max_x = pmax(year_2007, year_1952),
diff = year_2007 - year_1952,
diff_lab = sprintf("%+d", round(diff))
)
p_dumbbell <- ggplot(data = dat) +
aes(x = lifeExp, y = country, color = fct_rev(year)) +
geom_segment(
data = dat_wide,
aes(x = year_1952, xend = year_2007, y = country, yend = country),
color = "#AAAAAA", linewidth = 1
) +
geom_point(size = 3) +
geom_text(
mapping = aes(label = round(lifeExp)),
size = 2.5, vjust = -1, family = "kanit"
) +
geom_text(
data = dat_wide,
mapping = aes(x = max_x, label = diff_lab),
size = 2.5, hjust = 0,
position = position_nudge(x = 1),
color = "#AAAAAA", family = "kanit"
) +
scale_color_manual(
name = "Year", limits = c("1952", "2007"),
values = year_colors, guide = "none"
) +
scale_y_discrete(name = NULL) +
scale_x_continuous(name = NULL) +
labs(title = "LEBENSERWARTUNG", subtitle = long_subtitle) +
theme_nature()
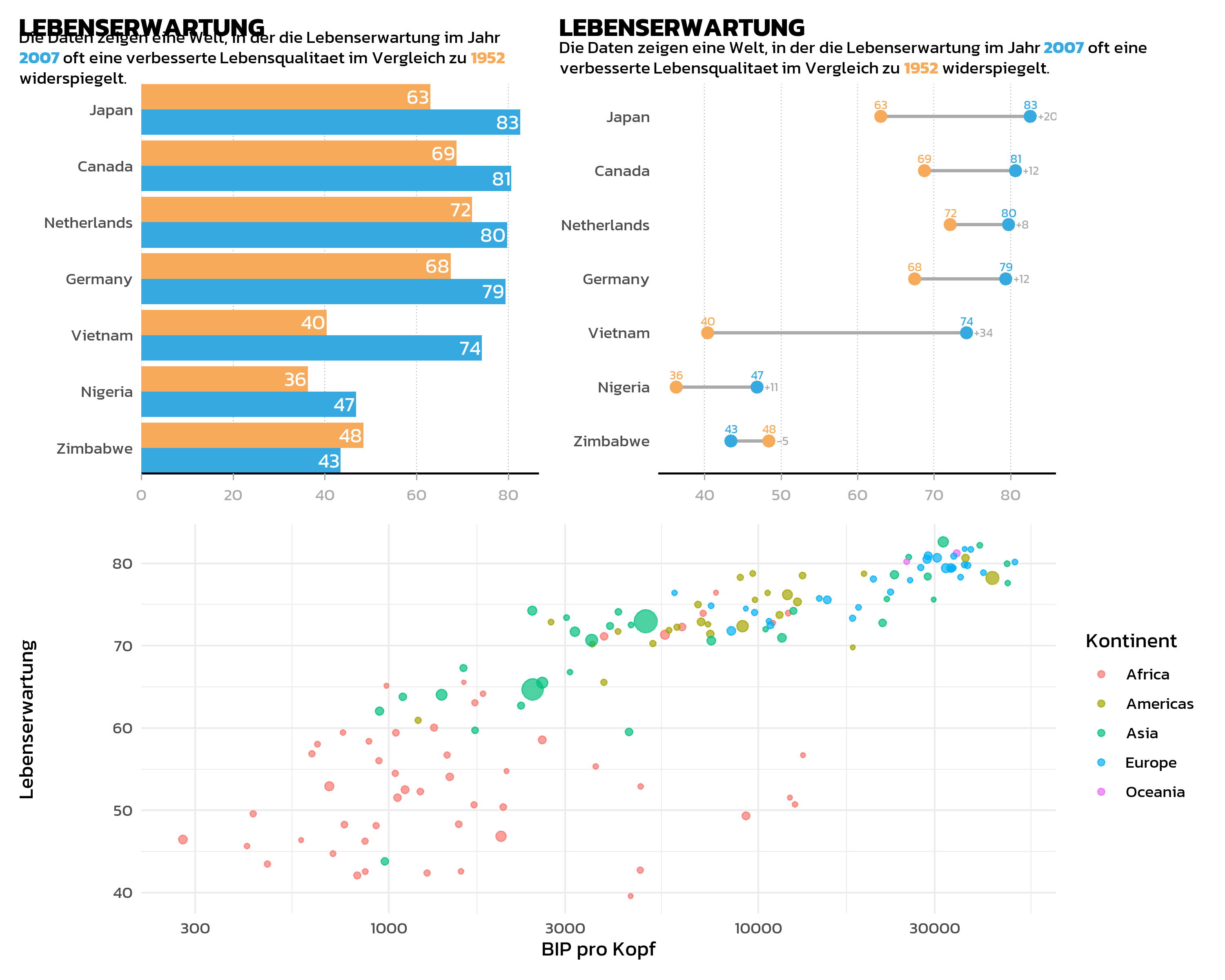
# Einfacher Scatter Plot fuer BIP
p_gdp <- ggplot(
data = gapminder::gapminder %>% filter(year == 2007),
aes(x = gdpPercap, y = lifeExp, size = pop, color = continent)
) +
geom_point(alpha = 0.7) +
scale_x_log10() +
scale_size_continuous(guide = "none") +
labs(x = "BIP pro Kopf", y = "Lebenserwartung", color = "Kontinent") +
theme_minimal(base_size = 12) +
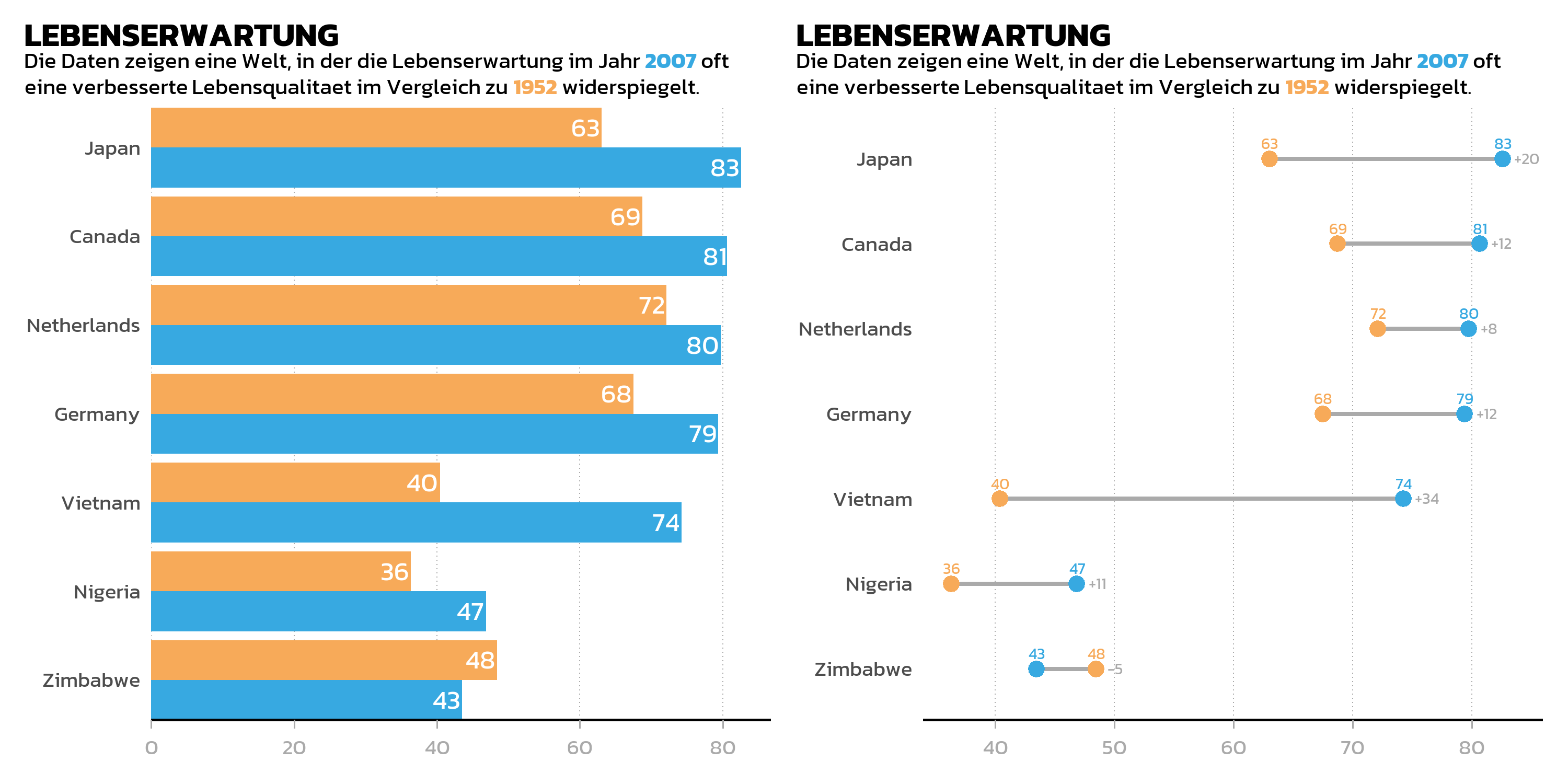
theme(text = element_text(family = "kanit"))Wir haben nun drei Plot-Objekte: p_bar (gruppiertes Balkendiagramm), p_dumbbell (Dumbbell Plot) und p_gdp (Streudiagramm).
Plots kombinieren
Der einfachste Weg, zwei Plots zu kombinieren, ist der +-Operator. Standardmaessig ordnet patchwork Plots nebeneinander an:
Nebeneinander: der |-Operator
Der |-Operator ist die explizite Version der Nebeneinander-Anordnung. Er verhaelt sich identisch zu + fuer zwei Plots, macht aber die Absicht in komplexen Layouts klarer:
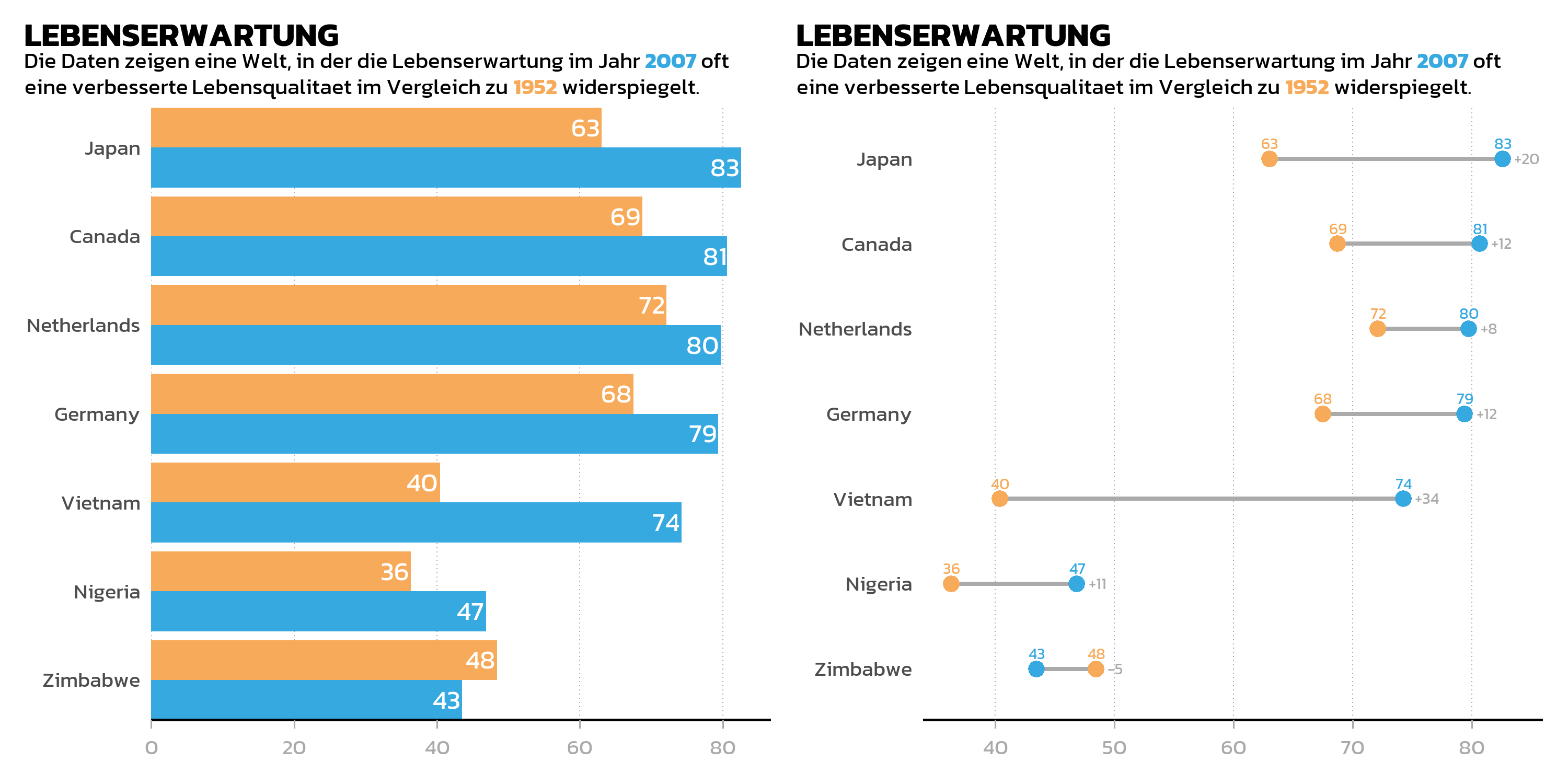
Uebereinander: der /-Operator
Der /-Operator platziert Plots uebereinander:
Operator-Praezedenz
Beim Kombinieren von Operatoren spielt die Praezedenz eine Rolle. Der /-Operator (Stapeln) bindet staerker als | (Nebeneinander), sodass p1 | p2 / p3 als p1 | (p2 / p3) interpretiert wird statt als (p1 | p2) / p3. Der +-Operator hat die niedrigste Praezedenz. In der Praxis bedeutet das: Man sollte immer Klammern verwenden, um das beabsichtigte Layout explizit zu machen — sich auf Praezedenzregeln zu verlassen fuehrt zu Ueberraschungen.
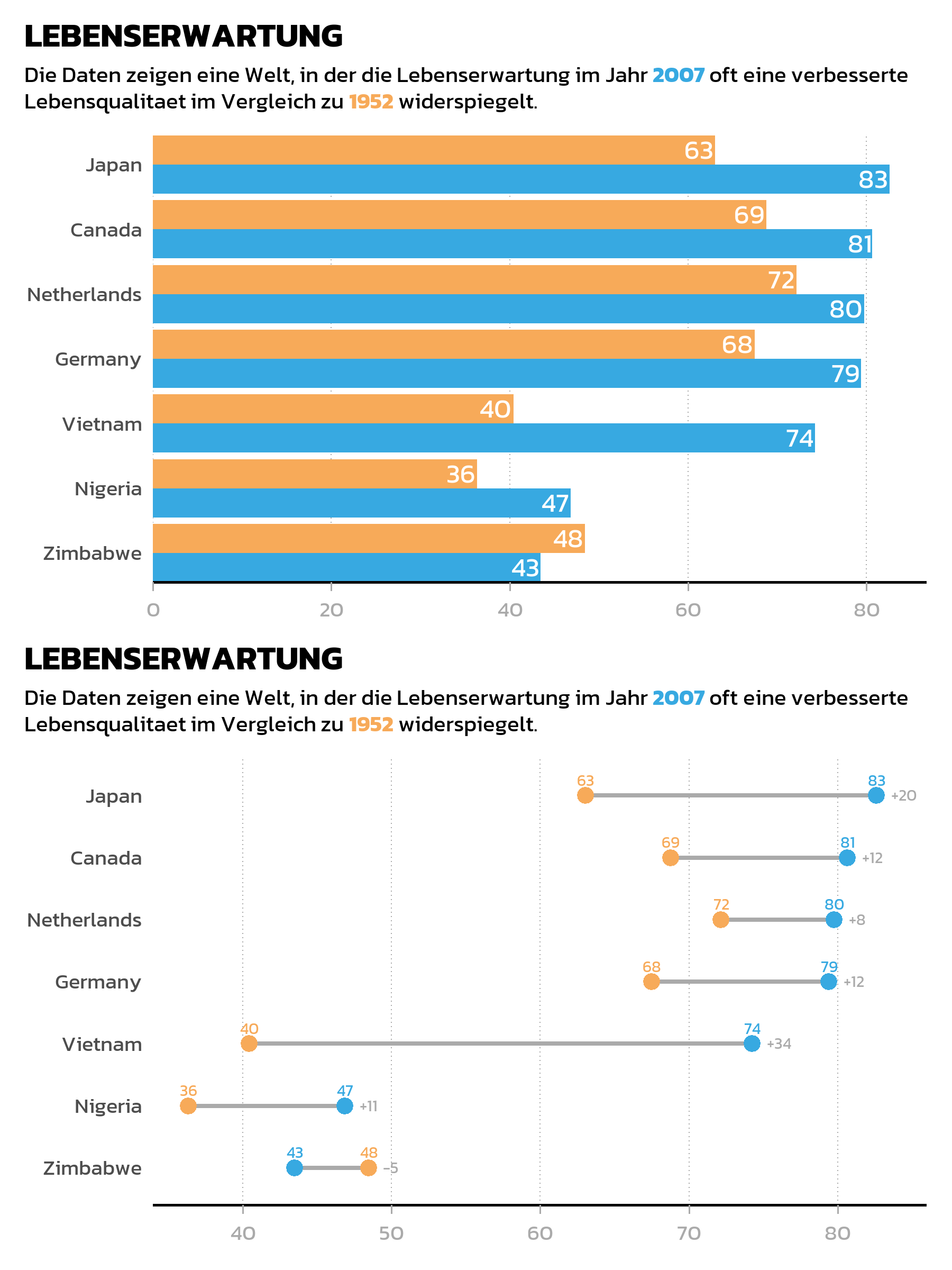
Verschachtelte Layouts
Klammern machen die Layout-Struktur explizit und lesbar. Zum Beispiel zwei Plots nebeneinander oben, mit einem dritten Plot ueber die volle Breite unten:
Layout-Steuerung
Die plot_layout()-Funktion bietet feingranulare Kontrolle ueber die Anordnung:
(p_bar | p_dumbbell) / p_gdp +
plot_layout(heights = c(2, 1))Wichtige Argumente:
-
widthsundheights: Relative Groessen von Spalten und Zeilen.heights = c(2, 1)macht die obere Reihe doppelt so hoch wie die untere. -
ncolundnrow: Erzwingt ein bestimmtes Gitterlayout. -
guides = "collect": Sammelt identische Legenden aus allen Plots und zeigt sie einmal. Besonders nuetzlich, wenn mehrere Plots dieselbe Farbskala teilen.
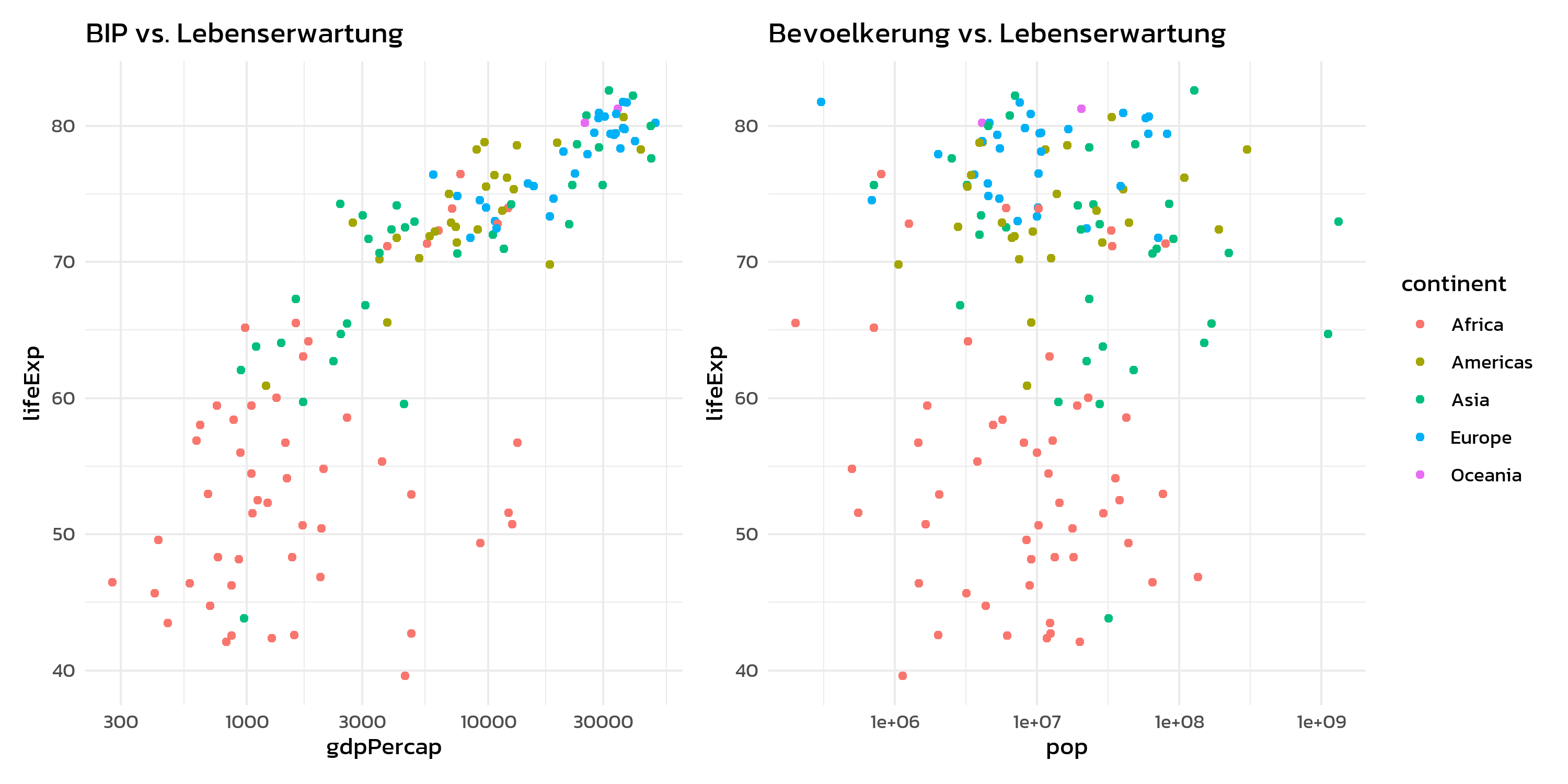
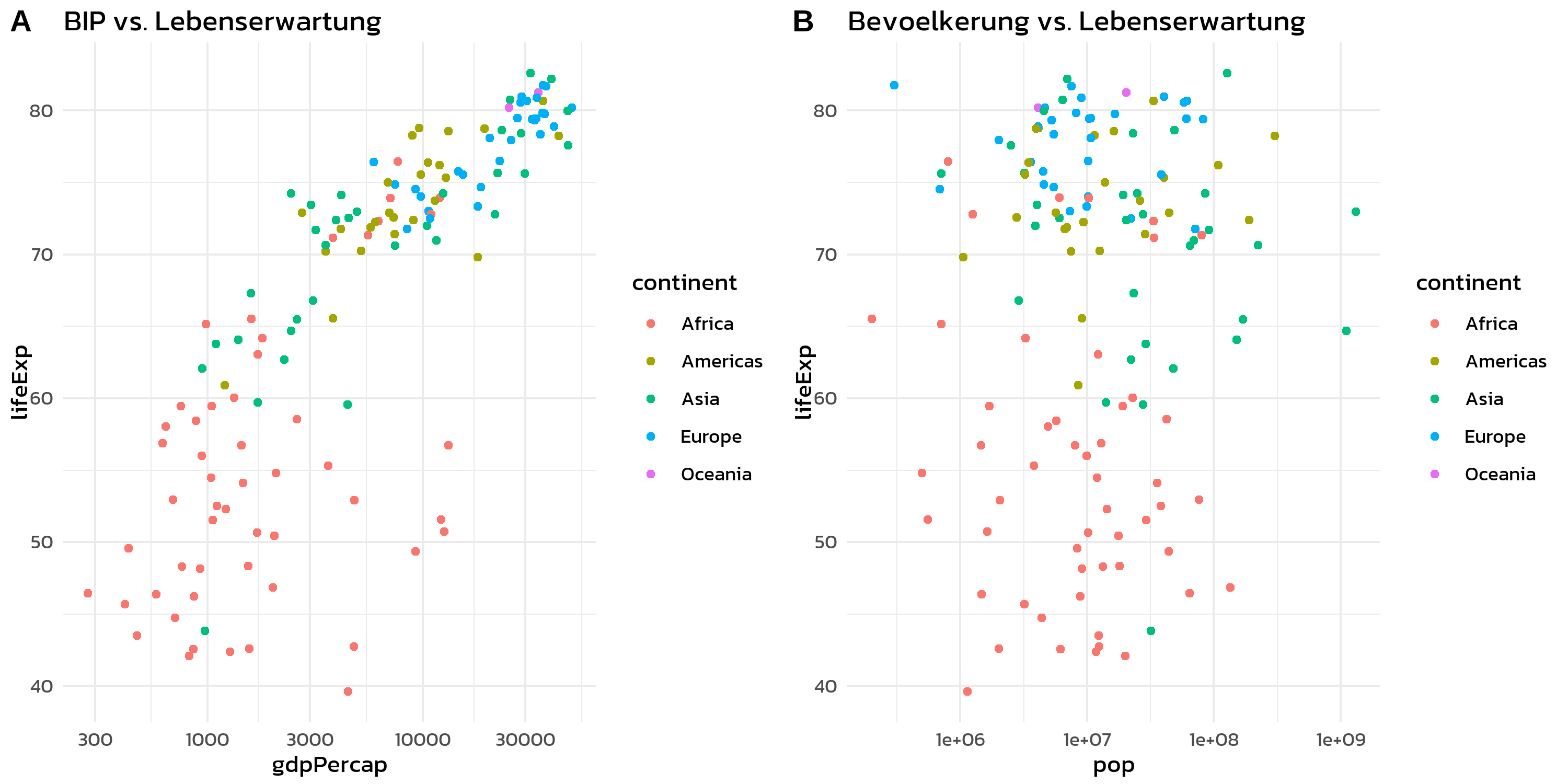
p1 <- ggplot(gapminder::gapminder %>% filter(year == 2007),
aes(x = gdpPercap, y = lifeExp, color = continent)) +
geom_point() + scale_x_log10() + theme_minimal(base_size = 11) +
theme(text = element_text(family = "kanit")) +
labs(title = "BIP vs. Lebenserwartung")
p2 <- ggplot(gapminder::gapminder %>% filter(year == 2007),
aes(x = pop, y = lifeExp, color = continent)) +
geom_point() + scale_x_log10() + theme_minimal(base_size = 11) +
theme(text = element_text(family = "kanit")) +
labs(title = "Bevoelkerung vs. Lebenserwartung")
p1 + p2 + plot_layout(guides = "collect")Ohne guides = "collect" wuerde jeder Plot seine eigene Kontinent-Legende zeigen - redundant und platzverschwendend.
Annotationen
plot_annotation() fuegt Titel, Untertitel, Quellenangaben und automatische Panel-Tags zur kombinierten Abbildung hinzu:
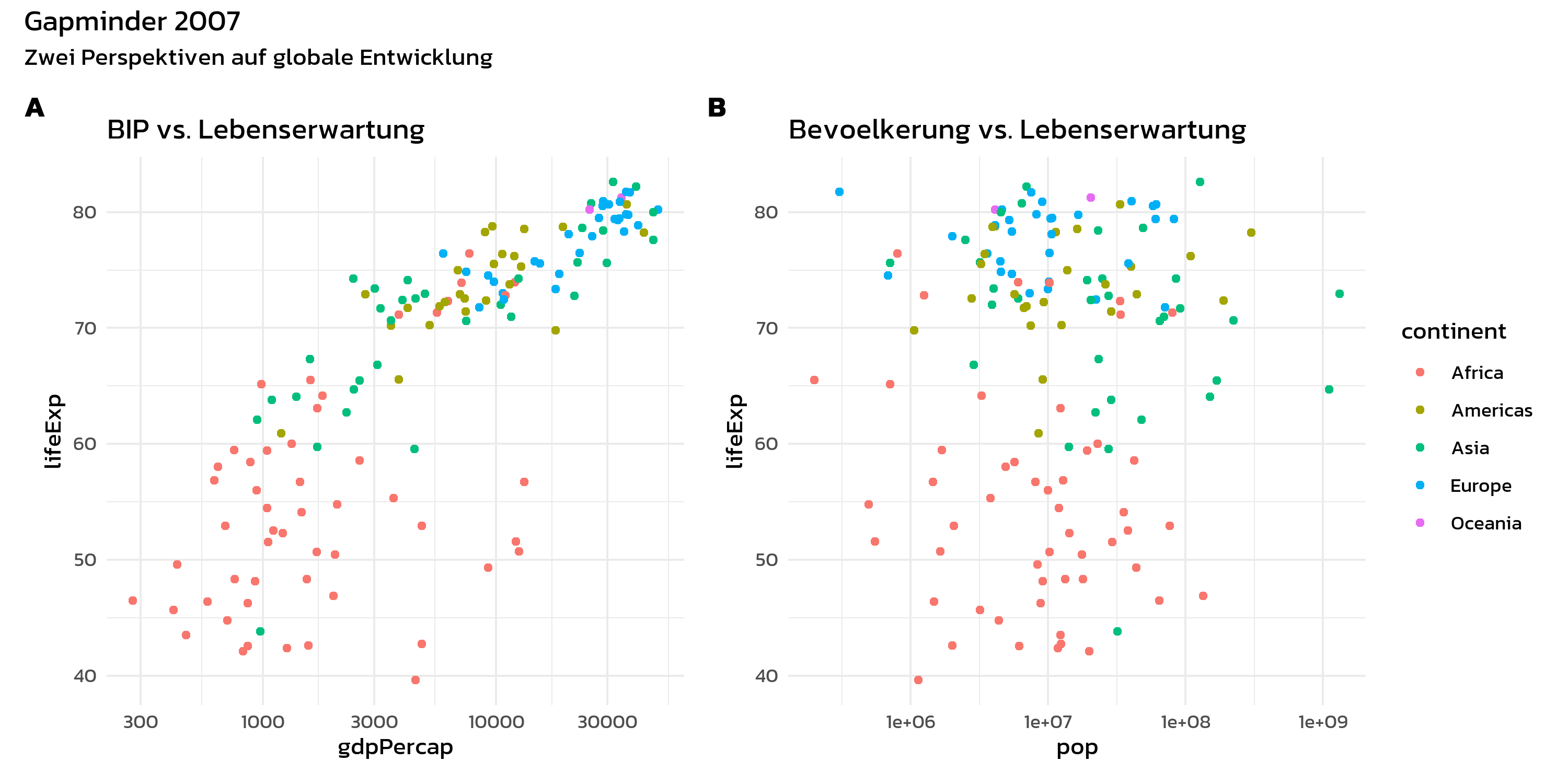
p1 + p2 +
plot_layout(guides = "collect") +
plot_annotation(
title = "Gapminder 2007",
subtitle = "Zwei Perspektiven auf globale Entwicklung",
tag_levels = "A"
) &
theme(
text = element_text(family = "kanit"),
plot.tag = element_text(face = "bold")
)Das tag_levels-Argument beschriftet Panels automatisch als “A”, “B”, “C” (oder “1”, “2”, “3”, “a”, “b”, “c”, “I”, “II”, “III”). Das ist essenziell fuer Journal-Abbildungen, in denen Panels im Text referenziert werden muessen.
Der &-Operator
Man beachte den &-Operator im letzten Beispiel. Das ist eine der nuetzlichsten Funktionen von patchwork:
-
+fuegt eine Theme-Aenderung nur zum letzten Plot hinzu -
&wendet eine Theme-Aenderung auf alle Plots in der Komposition an
Diese Unterscheidung ist wichtig, wenn man ein einheitliches Theme ueber alle Panels hinweg anwenden moechte:
Ueber patchwork hinaus: cowplot
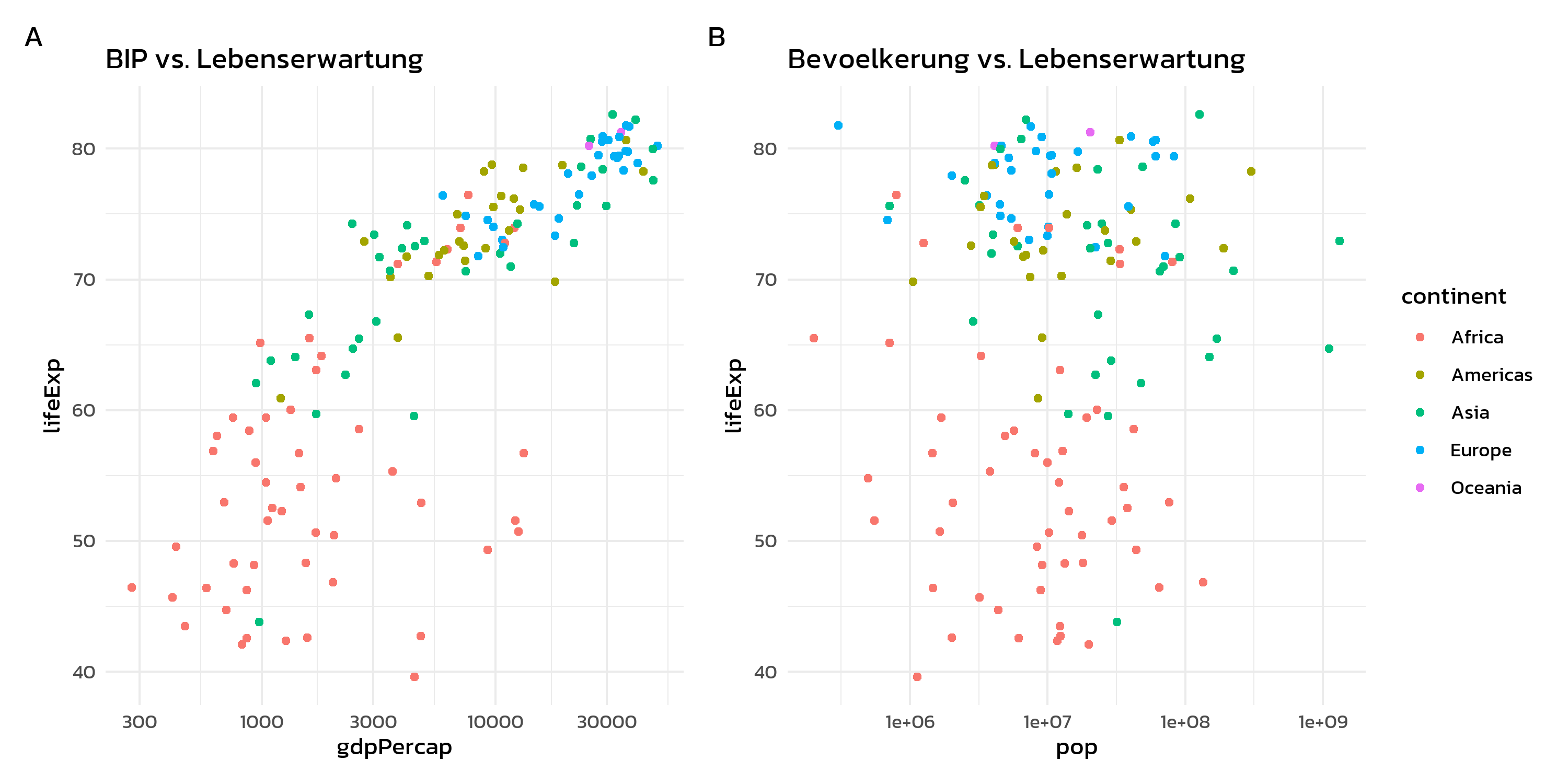
Das {cowplot}-Paket von Claus Wilke bietet ergaenzende Funktionalitaet zum Kombinieren von Plots. Waehrend patchwork bei gitterbasierten Layouts mit seiner Operatorsyntax glaenzt, punktet cowplot in zwei spezifischen Bereichen: automatische Panel-Beschriftungen und Inset-Plots.
Einfaches Gitter mit cowplot
Die cowplot::plot_grid()-Funktion arbeitet aehnlich wie patchworks +-Operator, bietet aber Panel-Beschriftungen direkt ueber das labels-Argument:
cowplot::plot_grid(p1, p2, labels = "AUTO")labels = "AUTO" erzeugt Grossbuchstaben-Labels (A, B, C, …), waehrend labels = "auto" Kleinbuchstaben liefert (a, b, c, …).
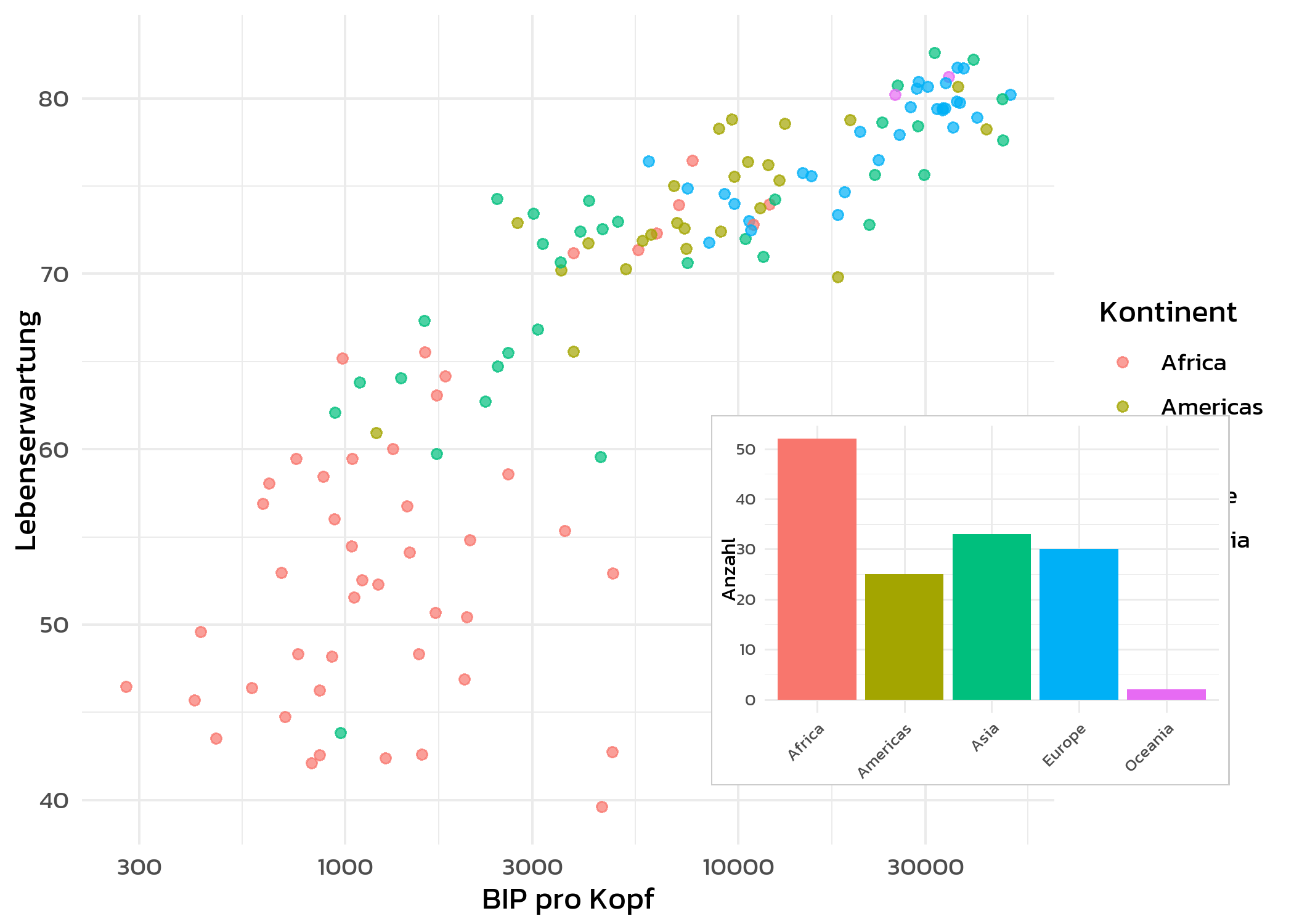
Inset-Plots
Eine Funktion, die patchwork nicht bietet, ist das Platzieren eines kleinen Plots innerhalb eines groesseren - ein Inset-Plot. Das ist nuetzlich, um ein vergroessertes Detail, eine zusammenfassende Statistik oder eine ergaenzende Ansicht innerhalb derselben Abbildung zu zeigen. Die Funktionen cowplot::ggdraw() und cowplot::draw_plot() machen das unkompliziert:
dat_2007 <- gapminder::gapminder %>% filter(year == 2007)
p_main <- ggplot(dat_2007, aes(x = gdpPercap, y = lifeExp, color = continent)) +
geom_point(alpha = 0.7) +
scale_x_log10() +
labs(x = "BIP pro Kopf", y = "Lebenserwartung", color = "Kontinent") +
theme_minimal(base_size = 12) +
theme(text = element_text(family = "kanit"))
p_inset <- ggplot(dat_2007, aes(x = continent, fill = continent)) +
geom_bar(show.legend = FALSE) +
labs(x = NULL, y = "Anzahl") +
theme_minimal(base_size = 8) +
theme(
text = element_text(family = "kanit"),
axis.text.x = element_text(angle = 45, hjust = 1),
plot.background = element_rect(fill = "white", color = "grey80")
)
cowplot::ggdraw(p_main) +
cowplot::draw_plot(p_inset, x = 0.55, y = 0.15, width = 0.4, height = 0.4)Die Argumente x, y, width und height in draw_plot() verwenden relative Koordinaten (0 bis 1), wobei (0, 0) die untere linke Ecke ist. Durch Anpassen dieser Werte positioniert und dimensioniert man den Inset-Plot innerhalb der Hauptabbildung.
Fuer die meisten Multi-Panel-Layouts bleibt patchwork aufgrund seiner saubereren Syntax und automatischen Ausrichtung die bessere Wahl. cowplot lohnt sich, wenn man Inset-Plots benoetigt oder das plot_grid()-Interface fuer einfache Nebeneinander-Anordnungen mit automatischen Labels bevorzugt.
Beide Werkzeuge erstellen Multi-Panel-Abbildungen, aber sie dienen unterschiedlichen Zwecken:
-
Facets (
facet_wrap(),facet_grid()): Gleicher Plottyp, gleiche Datenstruktur, aufgeteilt nach einer Gruppierungsvariable. Achsen werden geteilt oder individuell skaliert. Am besten fuer systematische Vergleiche innerhalb eines Datensatzes. - Patchwork: Verschiedene Plottypen, verschiedene Datensaetze oder verschiedene aesthetische Mappings. Jedes Panel ist ein voellig unabhaengiger ggplot. Am besten zum Kombinieren komplementaerer Sichten auf die Daten.
Eine gute Faustregel: Wenn man die Panels als “denselben Plot fuer verschiedene Gruppen” beschreiben kann, nimmt man Facets. Wenn die Panels grundlegend verschiedene Dinge zeigen, nimmt man patchwork.
Zitat
@online{schmidt2026,
author = {{Dr. Paul Schmidt}},
publisher = {BioMath GmbH},
title = {9. patchwork},
date = {2026-03-12},
url = {https://biomathcontent.netlify.app/de/content/ggplot2/09_patchwork.html},
langid = {de}
}